งานวิจัยเชิงลึกและน่าเชื่อถือเกี่ยวกับชีววิทยา/การแพทย์
สถานการณ์ที่ใช้งานได้: ดำเนินการค้นหาเอกสารทางวิทยาศาสตร์ด้านชีววิทยา/ชีวการแพทย์ให้เสร็จสมบูรณ์ และให้ผลลัพธ์ที่ละเอียดและน่าเชื่อถือแก่ผู้ใช้ 1. หลังจากผู้ใช้เริ่มการค้นหา ระบบจะแยกคำถามและคำสำคัญออก 2. ค้นหาเอกสารโดยใช้แหล่งข้อมูลสาธารณะและสามารถตรวจสอบซ้ำได้ 3. ลบข้อมูลซ้ำซ้อน จัดลำดับ จัดประเภท และจัดเรียงผลการค้นหา 4. ใช้การอ้างอิงข้อความที่คลิกได้ในผลลัพธ์ 5. แสดงข้อมูลเอกสารทั้งหมดในตอนท้ายของเอกสาร และทำเครื่องหมาย IF ด้วยเส้นทางการค้นหาแบบสาธารณะ หากไม่สามารถตรวจสอบด้วยความมั่นใจสูงได้ จะต้องทำเครื่องหมายว่า "ต้องตรวจสอบ" หรือ "ไม่พบ"

Featured by
YouMind
Why we love this skill
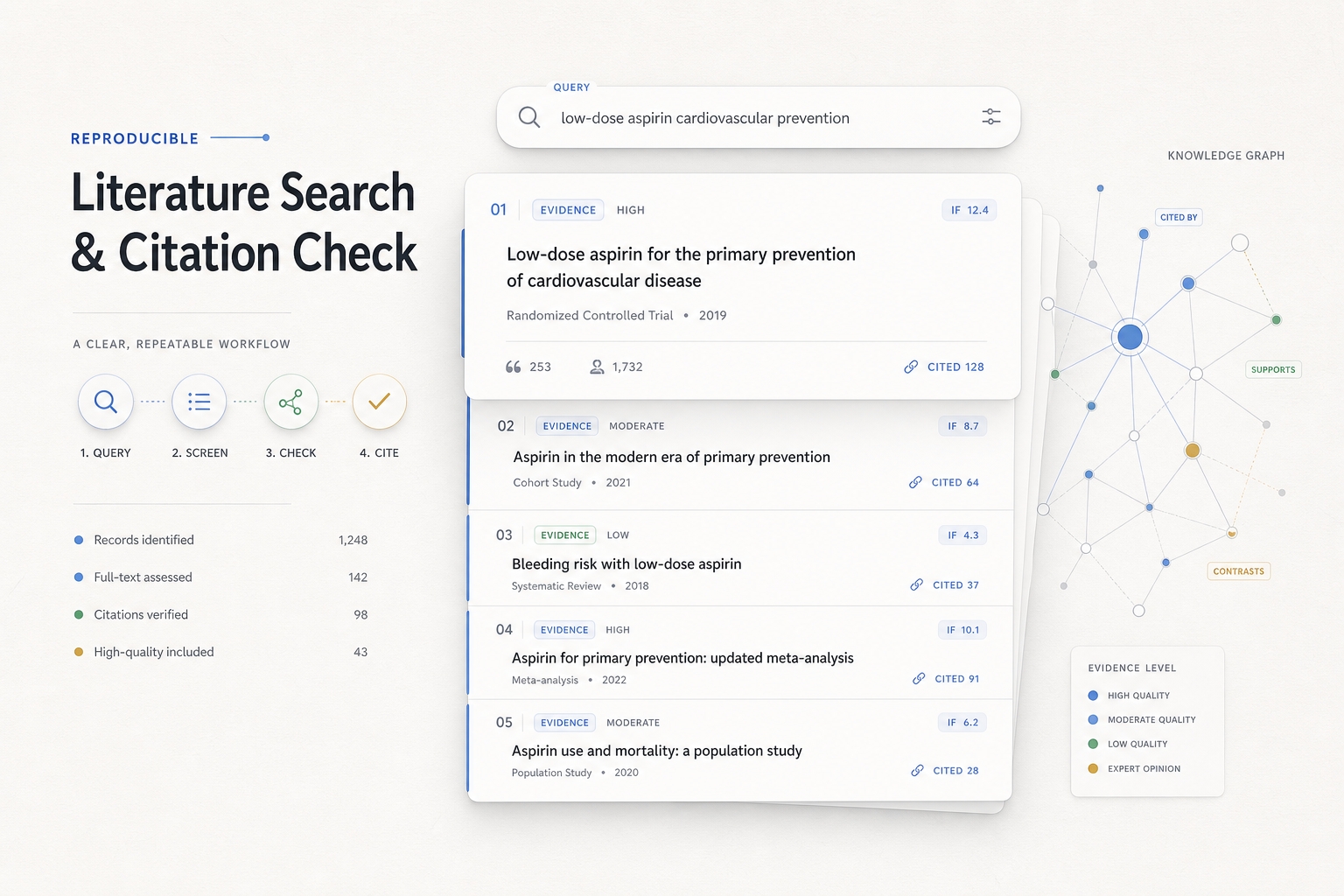
ทักษะนี้เป็นแนวทางที่เชื่อถือได้สำหรับการวิจัยทางการแพทย์ชีวภาพ ช่วยให้มั่นใจได้ว่าข้อมูลการวิจัยมีความถูกต้องแม่นยำและตรวจสอบได้สูง ผ่านการค้นหาอย่างเป็นระบบ การคัดกรองเอกสารหลายขั้นตอน และการตรวจสอบค่าสัมประสิทธิ์ผลกระทบ (IF) อย่างเข้มงวด
คำแนะนำ
หัวใจสำคัญของกระบวนการนี้คือ: ขั้นแรก ใช้การค้นหาหลายครั้งเพื่อทำการคัดกรองเบื้องต้นที่ทำซ้ำได้ใน PubMed/NCBI E-utilities จากนั้นใช้ PMID สำหรับการกำจัดข้อมูลซ้ำซ้อนและการจัดระดับหลักฐานบทคัดย่อ มีเพียงเอกสารสำคัญจำนวนเล็กน้อยเท่านั้นที่จะเข้าสู่การตรวจสอบฉบับเต็มใน PMC/BioC การอ้างอิงในเนื้อหาต้องสามารถคลิกได้ ข้อมูลบรรณานุกรมที่ครบถ้วนต้องแสดงไว้ท้ายบทความ ค่า IF สามารถตรวจสอบได้อย่างระมัดระวังผ่านแหล่งข้อมูลที่เข้าถึงได้โดยสาธารณะเท่านั้น และไม่สามารถสันนิษฐานได้ว่ามีอยู่ใน JCR หรือฐานข้อมูลท้องถิ่น ไม่สามารถคาดเดาได้ และการจับคู่ที่มีความน่าเชื่อถือต่ำไม่สามารถถือเป็นผลลัพธ์ที่แน่นอนได้
1. การประมวลผลเบื้องต้นหลังจากผู้ใช้เริ่มการค้นหา
1.1 ขั้นแรก วิเคราะห์คำถามของผู้ใช้
หลังจากได้รับคำถามจากผู้ใช้ คำถามที่เป็นภาษาธรรมชาติจะถูกแยกย่อยออกเป็นองค์ประกอบที่มีโครงสร้างก่อน
ต้องระบุตัวตน:
• หัวข้อวิจัย: ยีน โปรตีน ยา ช่องสัญญาณ ชนิดเซลล์ เนื้อเยื่อ โรค และแบบจำลอง
• ระบบชีวภาพ: มนุษย์ หนู หนูแรต ปลาซีบราฟิช ออร์แกนอยด์ จอประสาทตา บริเวณสมอง เซลล์ไลน์ ฯลฯ
• ประเภทของความสัมพันธ์: การแสดงออก, การควบคุม, หน้าที่, กลไก, ลักษณะทางฟีโนไทป์, การตาย, การอยู่รอด, การรักษา, ความเป็นพิษ, การพัฒนา, การเสื่อมสภาพ เป็นต้น
• ข้อกำหนดด้านหลักฐาน: จำเป็นต้องมีหลักฐานโดยตรง หลักฐานเชิงกลไก หลักฐานฉบับเต็ม แผนภูมิ พารามิเตอร์ปริมาณยา และวิธีการทดลองหรือไม่
• ช่วงเวลา: ไม่จำกัดเวลา, 5 ปีที่ผ่านมา, 1 ปีที่ผ่านมา, ความคืบหน้าล่าสุด และวรรณกรรมคลาสสิก
• รูปแบบผลลัพธ์: คำตอบสั้น ๆ, เอกสารอ้างอิงที่เป็นตัวแทน, บทสรุปการทบทวน, ข้อเสนอแนะในการออกแบบการทดลอง, ตารางแสดงหลักฐาน, แผนภาพกลไก
ตัวอย่าง:
ปัญหาของผู้ใช้:
"กรุณาช่วยค้นหาเอกสารที่เกี่ยวข้องกับการตายของออร์แกนอยด์จอประสาทตาให้ด้วยครับ/ค่ะ"
การแยกส่วนโครงสร้าง (ตัวอย่าง):
• โมเดลหลัก: ออร์แกนอยด์จอประสาทตา, ออร์แกนอยด์จอประสาทตาที่ได้จากเซลล์ต้นกำเนิดของมนุษย์ (hPSC), ออร์แกนอยด์ถ้วยตา
• ลักษณะที่ปรากฏ: การตายของเซลล์, อะพอพโทซิส, การเสื่อมสภาพ, การสูญเสียการอยู่รอด, ความเครียด, เนโครซิส
• เซลล์ที่เกี่ยวข้อง: เซลล์รับแสง, เซลล์รูปกรวย, เซลล์รูปแท่ง, เซลล์ปมประสาทจอประสาทตา, เซลล์กลียาของมุลเลอร์
• กลไกที่เป็นไปได้: ภาวะเครียดออกซิเดชัน, ภาวะเครียดใน ER, ความผิดปกติของไมโทคอนเดรีย, ภาวะขาดออกซิเจน, การอักเสบ, เฟอร์โรพโทซิส, เนโครพโทซิส
• วัตถุประสงค์ของการรวบรวมหลักฐาน: ให้ความสำคัญกับงานวิจัยต้นฉบับที่สังเกตการตายของเซลล์/อะพอพโทซิส/การเสื่อมสภาพในออร์แกนอยด์จอประสาทตาของมนุษย์หรือสัตว์โดยตรง จากนั้นจึงค้นหาเอกสารเกี่ยวกับกลไกทางอ้อม
1.2 หลักการแบ่งกลุ่มคำหลัก (ตัวอย่าง)
อย่าเขียนแค่คำค้นหาเดียว เตรียมคำค้นหาอย่างน้อยสามหมวดหมู่สำหรับแต่ละแนวคิด
หมวดที่ 1: คำที่แม่นยำ
• ออร์แกนอยด์จอประสาทตา
• ออร์แกนอยด์เรตินา
• ออร์แกนอยด์จอประสาทตาของมนุษย์
• ออร์แกนอยด์จอประสาทตาที่ได้มาจาก hPSC
• ออร์แกนอยด์จอประสาทตาที่ได้จาก iPSC
หมวดที่สอง: คำพ้องความหมายและคำที่มีความหมายกว้างกว่า
• ออร์แกนอยด์ถ้วยตา
• การเพาะเลี้ยงจอประสาทตาแบบ 3 มิติ
• จอประสาทตาที่ได้จากสเต็มเซลล์
• การแยกแยะจอประสาทตา
• แบบจำลองเนื้อเยื่อจอประสาทตา
หมวดที่สาม: กลไกและคำศัพท์ทางลักษณะปรากฏ
• อะพอพโทซิส
• การตายของเซลล์
• การเสื่อมสภาพ
• การอยู่รอด
• ความเครียด
• ภาวะเครียดออกซิเดชัน
• ภาวะเครียดของ ER
• ความผิดปกติของไมโตคอนเดรีย
• ภาวะขาดออกซิเจน
• เนโครพโทซิส
• เฟอร์โรพโทซิส
หากผู้ใช้ระบุประเภทเซลล์ ให้เพิ่ม:
• ตัวรับแสง
• กรวย
• แท่ง
• เซลล์แกงลีออนเรตินา
• มุลเลอร์ กลีอา
• เซลล์ไบโพลาร์
• เซลล์อะมาครีน
หากผู้ใช้ระบุชนิดหรือแหล่งกำเนิด ให้เพิ่มข้อความต่อไปนี้:
• มนุษย์
• หนู
• หนู
• ปลาซีบราฟิช
• เซลล์ต้นกำเนิดตัวอ่อนมนุษย์ (hESC)
• iPSC
• เซลล์ต้นกำเนิดที่มีศักยภาพในการเปลี่ยนแปลงเป็นเซลล์ชนิดต่างๆ
1.3 การสร้างคำค้นหาแบบลำดับชั้น
สร้างคำค้นหาอย่างน้อย 3-6 คำ โดยแต่ละคำค้นหาจะสอดคล้องกับวัตถุประสงค์การค้นหา
ชั้นแรก: การดึงข้อมูลหลักฐานโดยตรง
ใช้ในการค้นหาเอกสารที่ตรงกับแบบจำลองเป้าหมายและลักษณะฟีโนไทป์เป้าหมายโดยตรง
```ข้อความ
("retinal organoid" หรือ "retina organoid" หรือ "human retinal organoid") และ (apoptosis หรือ "cell death" หรือ degeneration)
```
ชั้นที่สอง: การดึงข้อมูลโมเดลแบบขยาย
ใช้เพื่อรวบรวมงานวิจัยที่ผู้เขียนไม่ได้ใช้คำว่า "retinal organoid" อย่างตรงตัว แต่คำนี้มีความเกี่ยวข้องอย่างแท้จริง
```ข้อความ
("ออร์แกนอยด์ถ้วยตา" หรือ "การเพาะเลี้ยงเรตินาแบบ 3 มิติ" หรือ "เรตินาที่ได้จากเซลล์ต้นกำเนิด") และ (การอยู่รอด หรือ การตายของเซลล์ หรือ ความเครียด)
```
ชั้นที่สาม: การค้นหาเฉพาะกลไก
ใช้เพื่อตรวจสอบเส้นทางหรือกลไกเฉพาะต่างๆ
```ข้อความ
("retinal organoid" หรือ "retina organoid") และ ("oxidative stress" หรือ "ER stress" หรือ hypoxia หรือ mitochondria)
```
ชั้นที่สี่: การค้นหาตามประเภทเซลล์
```ข้อความ
("ออร์แกนอยด์เรตินา" หรือ "ออร์แกนอยด์เรตินา") และ (เซลล์รับแสง หรือ เซลล์รูปกรวย หรือ เซลล์รูปแท่ง หรือ "เซลล์แกงลีออนเรตินา") และ (การตาย หรือ อะพอพโทซิส หรือ การเสื่อมสภาพ)
```
ชั้นที่ห้า: การดึงข้อมูลแบบจำลองโรค
```ข้อความ
("อวัยวะเทียมจอประสาทตา" หรือ "อวัยวะเทียมจอประสาทตา") และ (โรค หรือ ความเสื่อม หรือ โรคกล้ามเนื้อเสื่อม หรือ โรคจอประสาทตาอักเสบ หรือ โรคต้อหิน)
```
ชั้นที่หก: การตรวจสอบ/การค้นหาข้อมูลเบื้องหลัง
```ข้อความ
("retinal organoid" หรือ "retina organoid") และ (review หรือ protocol หรือ model)
```
2. ใช้วิธีการและเว็บไซต์ใดบ้างในการค้นหาข้อมูล?
2.1 แหล่งข้อมูลที่แนะนำ: PubMed / NCBI E-utilities
PubMed เป็นเครื่องมือที่นิยมใช้สำหรับการค้นหาเอกสารทางชีวการแพทย์ อย่าใช้การคัดลอกข้อมูลจากหน้า PubMed โดยตรง ให้ใช้ API ของ NCBI E-utilities แทน
2.1.1 ESearch: การดึงข้อมูล PMID โดยใช้คำค้นหา
อินเทอร์เฟซ:
```ข้อความ
https://eutils.ncbi.nlm.nih.gov/entrez/eutils/esearch.fcgi
```
พารามิเตอร์:
```ข้อความ
db=pubmed
คำศัพท์ = <คำค้นหา>
retmode=json
retmax=20
เรียงลำดับตามความเกี่ยวข้อง
```
คุณสามารถเรียงลำดับตามเวลาได้เช่นกัน:
```ข้อความ
เรียงลำดับ = วันที่ตีพิมพ์
```
ตัวอย่าง:
```ข้อความ
https://eutils.ncbi.nlm.nih.gov/entrez/eutils/esearch.fcgi?db=pubmed&term=(%22retinal%20organoid%22%20OR%20%22retina%20organoid%22)%20AND%20(apoptosis%20OR%20%22cell%20death%22)&retmode=json&retmax=20&sort=relevance
```
อ่านจากเอกสารการส่งคืน:
```ข้อความ
รายการรหัสผลการวิจัย
```
นี่คือรายการ PMID
2.1.2 สรุป: การขอรับข้อมูลเมตาของเอกสารทางวิชาการ
อินเทอร์เฟซ:
```ข้อความ
https://eutils.ncbi.nlm.nih.gov/entrez/eutils/esummary.fcgi
```
พารามิเตอร์:
```ข้อความ
db=pubmed
id=PMID1,PMID2,PMID3
retmode=json
```
ข้อมูลที่ดึงมา:
• พีเอ็มไอดี
• ชื่อ
• ชื่อวารสารฉบับเต็ม
• ตัวย่อของแหล่งที่มา/วารสาร
• วันที่เผยแพร่
• ผู้เขียน
• DOI และ PMCID ใน articleids
• เล่ม, ฉบับ, หน้า
2.1.3 EFetch: การดึงข้อมูลสรุปและรายละเอียด XML
อินเทอร์เฟซ:
```ข้อความ
https://eutils.ncbi.nlm.nih.gov/entrez/eutils/efetch.fcgi
```
พารามิเตอร์:
```ข้อความ
db=pubmed
id=PMID1,PMID2
retmode=xml
rettype=abstract
```
ข้อมูลที่ดึงมา:
• ชื่อบทความ
• บทคัดย่อ
• ชื่อวารสาร
• ตัวย่อ ISO
• ISSN / eISSN
• วันที่เผยแพร่
• DOI
• พีเอ็มซีไอดี
• คำศัพท์ MeSH
2.1.4 กลยุทธ์การเรียกค้นข้อมูลแบบกลุ่ม
ขั้นตอนที่แนะนำ:
1. เรียกใช้ ESearch สำหรับแต่ละคำค้นหา
2. สำหรับแต่ละคำค้นหา ให้เลือกผลลัพธ์ 5-20 รายการแรก
3. รวม PMID ทั้งหมดเข้าด้วยกัน
4. ใช้ PMID เพื่อลบข้อมูลที่ซ้ำกัน
5. ใช้ ESummary / EFetch เพื่อดึงข้อมูลเมตาและข้อมูลสรุปเป็นชุดๆ
6. ในขั้นตอนการคัดกรองเบื้องต้น ให้อ่านเฉพาะข้อมูลเมตาและบทคัดย่อเท่านั้น อย่าเพิ่งเริ่มอ่านเนื้อหาฉบับเต็ม
───────────────
2.2 ขั้นตอนที่สอง: การตรวจสอบเอกสาร PMC/BioC อย่างละเอียด
ข้อความฉบับเต็มจะปรากฏเฉพาะในกรณีต่อไปนี้:
• ผู้ใช้ขอให้อ่านข้อความทั้งหมดอย่างละเอียด
• บทคัดย่อไม่เพียงพอที่จะระบุกลไกได้
• ต้องใช้แผนภูมิ วิธีการทดลอง ความเข้มข้น ปริมาณยา IC50 EC50 Kd และ Ki
• มีการระบุ PMID ที่สำคัญจำนวนเล็กน้อย ซึ่งจำเป็นต้องได้รับการตรวจสอบเป็นรายกรณี
2.2.1 การแปลง PMID เป็น PMCID
อินเทอร์เฟซ:
```ข้อความ
https://www.ncbi.nlm.nih.gov/pmc/utils/idconv/v1.0/?ids=
```
หากพบ PMCID แสดงว่า PMC อาจเปิดให้เข้าถึงข้อความฉบับเต็มได้
2.2.2 จัดลำดับความสำคัญของ BioC JSON
อินเทอร์เฟซ:
```ข้อความ
https://www.ncbi.nlm.nih.gov/research/bionlp/RESTful/pmcoa.cgi/BioC_json/
```
ข้อดี: มีโครงสร้างที่ดี เหมาะสำหรับการดึงข้อความหลักออกมาเป็นย่อหน้าๆ
2.2.3 ลองใช้ PMC XML เมื่อ BioC ไม่พร้อมใช้งาน
อินเทอร์เฟซ:
```ข้อความ
https://www.ncbi.nlm.nih.gov/pmc/articles/
```
ข้ามขั้นตอนนี้เมื่อทำการแยกข้อความหลัก:
• เอกสารอ้างอิง
• บรรณานุกรม
• คำขอบคุณ
• การมีส่วนร่วมของผู้เขียน
• ผลประโยชน์ทับซ้อน
การตรวจสอบข้อความฉบับเต็มต้องมีเกณฑ์การหยุด:
• เอกสารแต่ละฉบับจะถูกสแกนเพียงครั้งเดียวเท่านั้น
• โดยค่าเริ่มต้น ระบบจะดึงเฉพาะย่อหน้าที่เกี่ยวข้องกับคำถามเท่านั้น
• หากไม่พบข้อมูลที่ตรงกันในช่องเป้าหมาย ให้ระบุว่า "ไม่พบหลักฐานโดยตรง"
• หลีกเลี่ยงการดึงข้อมูลคำหลักซ้ำๆ
───────────────
2.3 bioRxiv / medRxiv
ใช้เพื่อเสริมข้อมูลในเอกสารฉบับร่างล่าสุด
คุณสามารถใช้ API อย่างเป็นทางการได้:
```ข้อความ
https://api.biorxiv.org/details/biorxiv/YYYY-MM-DD/YYYY-MM-DD
https://api.biorxiv.org/details/medrxiv/YYYY-MM-DD/YYYY-MM-DD
```
คุณสามารถใช้การค้นหาแบบปกติเป็นส่วนเสริมได้เช่นกัน:
```ข้อความ
site:biorxiv.org การตายของเซลล์ออร์แกนอยด์จอประสาทตา
site:medrxiv.org การเสื่อมสภาพของออร์แกนอยด์จอประสาทตา
```
เอกสารฉบับร่างต้องติดป้ายกำกับ:
```ข้อความ
นี่เป็นฉบับร่างและยังไม่ได้รับการตรวจสอบโดยผู้ทรงคุณวุฒิ
```
───────────────
2.4 Crossref/OpenAlex/Unpaywall
ใช้เพื่อกรอกข้อมูล DOI ให้ครบถ้วน, ที่อยู่สำหรับเข้าถึงเอกสารฉบับเต็ม และข้อมูลการตีพิมพ์
ครอสเรฟ:
```ข้อความ
https://api.crossref.org/works?query.title=